Sobre la nueva variante detectada en Reino Unido de SARS-CoV-2/COVID-19, algunos comentarios en base al gran trabajo de @arambaut @pathogenomenick @EvolveDotZoo @robertson_lab @alecarabo @erikmvolz et al y el consorcio
https://www.cogconsortium.uk/
(hilo)
https://www.cogconsortium.uk/
(hilo)
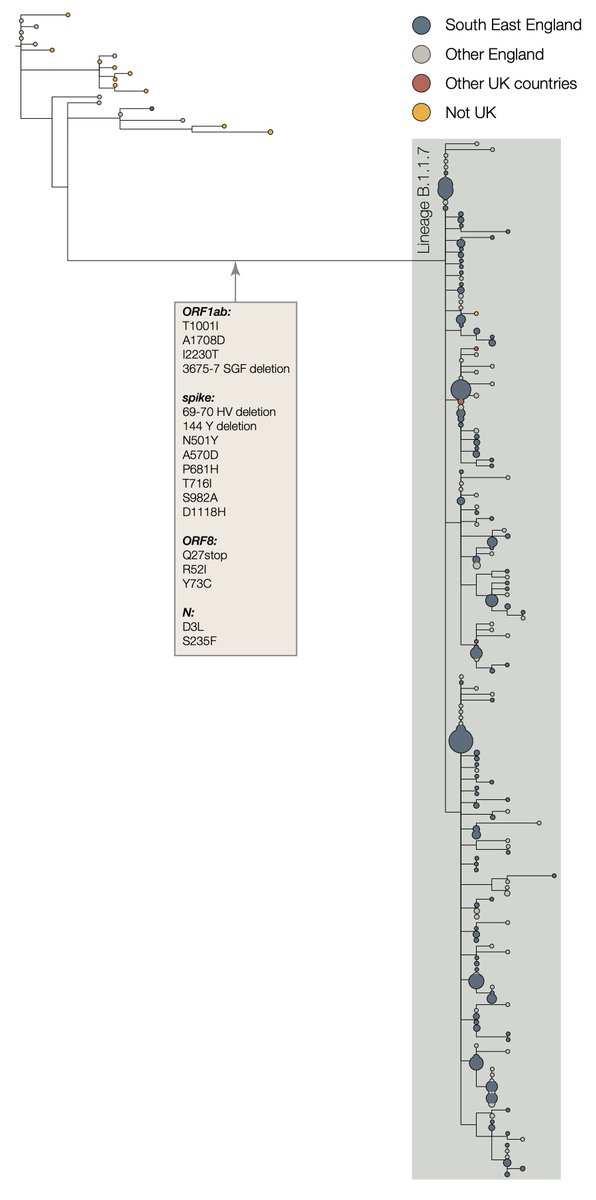
El equipo de vigilancia genómica COG-Reino Unido detectó un cluster filogenético distinto (llamado linaje B.1.1.7). Este cluster ha estado creciendo rápidamente durante las últimas 4 semanas y extendido en Reino Unido, lo que indica una mayor propagación. https://virological.org/t/preliminary-genomic-characterisation-of-an-emergent-sars-cov-2-lineage-in-the-uk-defined-by-a-novel-set-of-spike-mutations/563
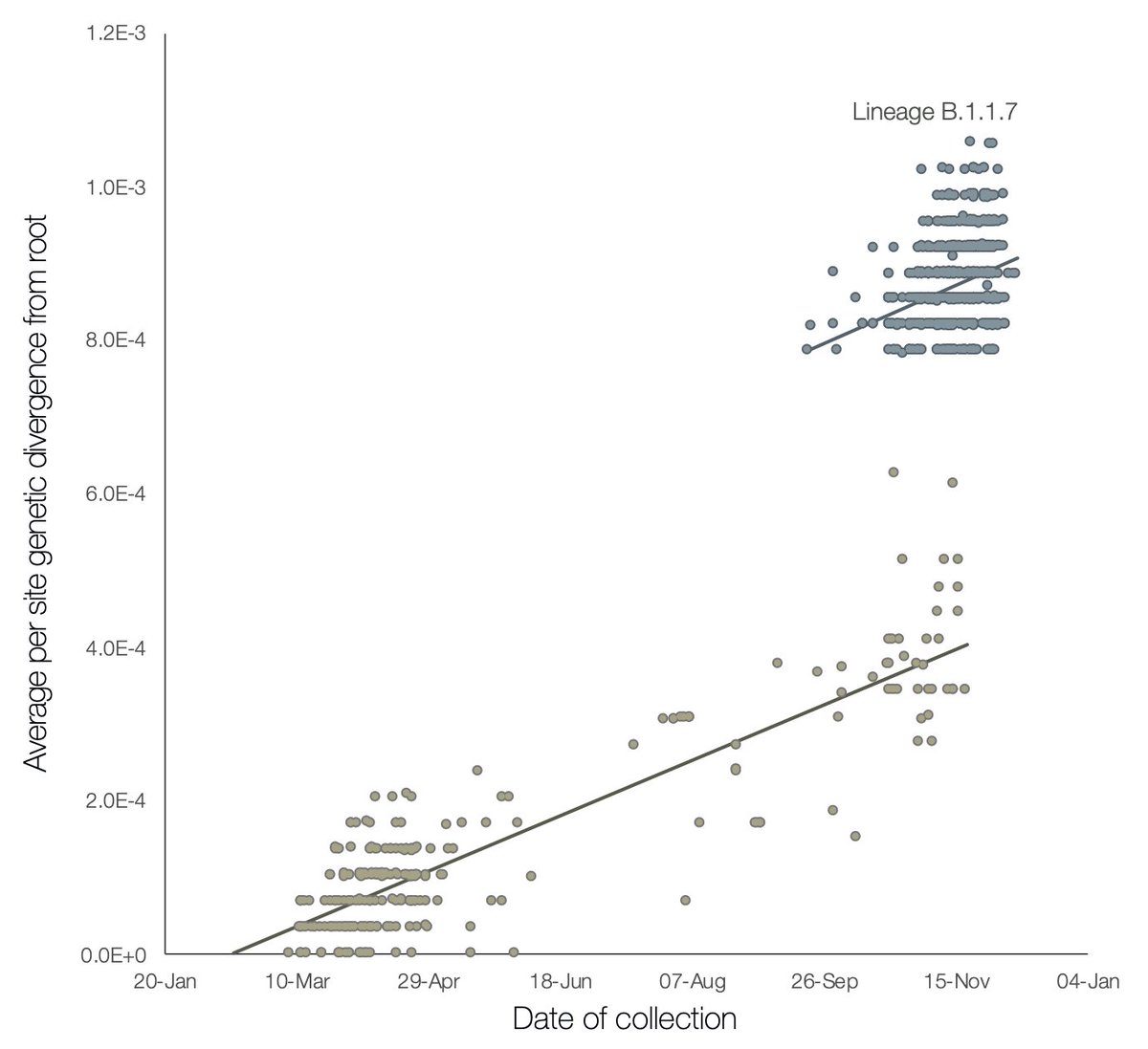
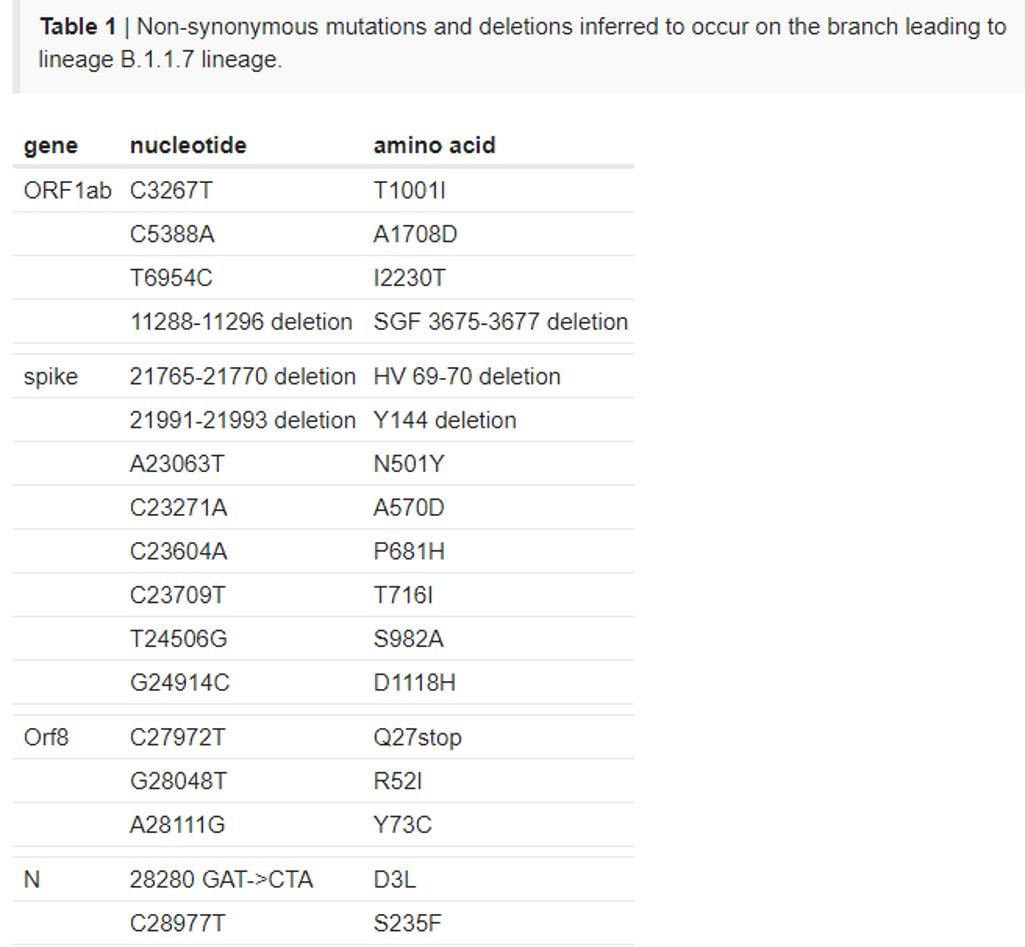
El linaje B.1.1.7 tiene un número mayor de lo habitual de cambios genéticos del virus. LA presencia de 14 cambios de aminoácidos específicos del linaje antes de su detección no tiene precedentes, hasta la fecha, en los datos genómicos del virus a nivel global para COVID-19.
Los linajes circulantes de SARS-CoV-2 acumulan mutaciones de nucleótidos a una tasa de ca. 1-2 mutaciones por mes. Sin embargo se observó una mayor tasa de evolución molecular en la rama filogenética inmediatamente ancestral a B.1.1.7.
Los cambios de nucleótidos observados en este linaje alteran predominantemente los aminoácidos (14 mutaciones no sinónimas y 3 deleciones) en contraste con solo 6 mutaciones sinónimas. Esto sugiere un proceso que involucra evolución molecular adaptativa.
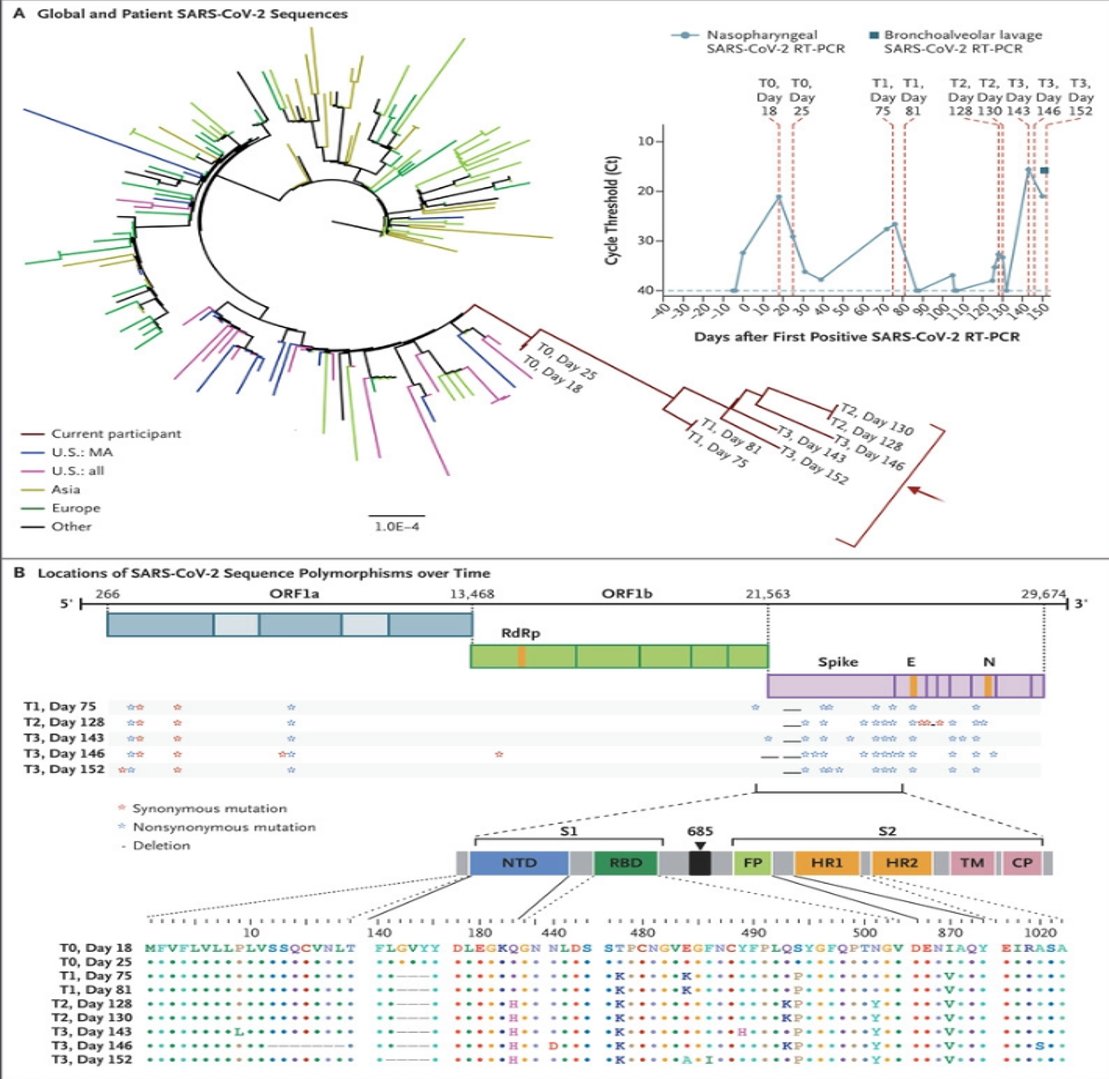
En estudios de pacientes inmunodeficientes o inmunosuprimidos que están crónicamente infectados con SARS-CoV-2 se han reportado altas tasas de acumulación de mutaciones durante períodos cortos de tiempo. https://www.nejm.org/doi/full/10.1056/NEJMc2031364
Su secuenciación reveló un número inusual y grande de mutaciones por deleción y alta proporción de cambios no sinónimos. La dinámica evolutiva y las presiones selectivas sobre la población de virus intrapaciente son muy diferentes a las experimentadas en la infección típica.
Si la terapia con anticuerpos/suero convaleciente se administra después de mucho tiempo de infección, la población de virus puede ser inusualmente grade y diversa cuando se aplica presión selectiva, facilitando la rápida fijación de múltiples cambios. https://www.cell.com/cell/fulltext/S0092-8674(20)31456-2
La divergencia genética inusual del linaje B.1.1.7 puede haber resultado de la evolución del virus en un individuo crónicamente infectado. Estas infecciones y su transmisión son raras pero probables con alta circulación viral o a nivel intra-hospitalario. https://doi.org/10.1101/2020.12.05.20241927
Entre las mutaciones identificadas en B.1.1.7 muchas involucran la proteína S, como 501, un residuo clave en el dominio de unión al receptor (RBD). Datos experimentales sugieren que la mutación N501Y aumenta la afinidad de S con el receptor ACE2 https://www.sciencedirect.com/science/article/pii/S0092867420310035
N501Y se ha asociado con una mayor infectividad y virulencia en un modelo de ratón, observándose mayor infectividad en el pulmón que condujo a neumonía intersticial y respuestas inflamatorias en ratones jóvenes/adultos luego de inoculación intranasal. https://science.sciencemag.org/content/369/6511/1603
También se detectó P681H, parte de la inserción que crea un sitio de escisión de furina entre S1 y S2 en SARS-CoV-2, que promueve la entrada a las células epiteliales respiratorias y la transmisión en modelos animales. P681H y N501Y 1ra vez juntas acá. https://pubmed.ncbi.nlm.nih.gov/32362314/
También presente la deleción de dos aminoácidos en los sitios 69-70 en S. Presente en alta frecuencia y múltiples linajes como en visón en Dinamarca con Y453F RBD, y en humanos con N439K RBD, facilitando el escape de terapias con anticuerpos https://www.biorxiv.org/content/10.1101/2020.11.19.389916v1
Fuera de S se observó una mutación ORF8 Q27 que trunca la proteína ORF8. La delecion de ORF8 se asoció con una infección clínica más leve y menos inflamación posterior a la infección en Singapur. https://www.thelancet.com/journals/lancet/article/PIIS0140-6736(20)31757-8/fulltext
Finalmente aparecieron 6 mutaciones sinónimas 5 en ORF1ab (C913T, C5986T, C14676T, C15279T, C16176T), y una en el gen M (T26801C). Este nuevo linaje tan divergente requiere una urgente caracterización de laboratorio y vigilancia genómica en todo el mundo. https://twitter.com/canardbruno/status/1340593532546015233
Algo análogo está sucediendo en África, donde está emergiendo la variante denominada 501.V2 dominante en Sudáfrica. La evidencia sugiere fuertemente que la segunda ola actual que están experimentando está siendo impulsada por esta nueva variante. https://twitter.com/DrZweliMkhize/status/1339970259332325383
Los médicos han proporcionado evidencia anecdótica de un cambio en el cuadro clínico epidemiológico. La carga viral más alta detectada en hisopados podría estar asociada a una mayor eficiencia de transmisión. https://twitter.com/DrZweliMkhize/status/1339976651908804608
Es imprescindible testear estas variantes. Las variantes emergentes deben analizarse contra sueros de individuos recuperados y vacunados para probar efectos antigénicos y confirmar respuestas neutralizantes. https://twitter.com/firefoxx66/status/1340359989395861506
Sin embargo, hasta tanto surjan evidencias adicionales no se espera que estas variantes reduzcan significativamente la eficacia de las vacuna en el 2021. https://twitter.com/trvrb/status/1340410010598174721
Las mutaciones únicas generalmente tienen bajos impactos en las respuestas inmunes policlonales. La fuerte respuesta inmune a las vacunas de ARNm sugiere que se necesitaría un gran cambio antigénico para reducir significativamente su eficacia. https://twitter.com/trvrb/status/1340410014255652865
Pero los coronavirus estacionales evolucionan para escapar de la neutralización mediada por anticuerpos: es decir las "reinfecciones" por coronavirus no ocurren por respuestas inmunes no duraderas, sino porque los virus evolucionan para evadirlas. https://twitter.com/jbloom_lab/status/1339939720558563328
Es decir que es importante el impacto de la circulación viral en su evolución. Permitir que las infecciones se propaguen es darle a SARS-CoV-2 la oportunidad de mutar más allá de las fronteras. Si un país falla, afectará a todos. https://twitter.com/EckerleIsabella/status/1340432688491212800
Algo análogo está sucediendo en África, donde está emergiendo la variante denominada 501.V2 que se ha vuelto dominante en Sudáfrica. La evidencia sugiere fuertemente que la segunda ola actual está siendo impulsada por esta nueva variante. https://twitter.com/DrZweliMkhize/status/1339970259332325383
Los médicos han proporcionado evidencia anecdótica de un cambio en el cuadro clínico epidemiológico. La carga viral más alta detectada en hisopados podría estar asociada a una mayor eficiencia de transmisión. https://twitter.com/DrZweliMkhize/status/1339976651908804608
Estamos avanzando hacia la fase de la pandemia donde la evolución puede jugar un papel en los efectos y es inevitable que haya una proliferación de especulaciones y opiniones en torno a la evolución del virus https://twitter.com/ArisKatzourakis/status/1340615011425787904
Todo esto es que ya sabemos, y lo que sabemos que no sabemos, es solo posible debido al gran trabajo en abierto en tiempo real sobre genómica viral de investigadores de todo el planeta https://twitter.com/ewanbirney/status/1340358445384523785
¿Querés saber más sobre cómo influye la evolución de patógenos en la dinámica epidémica (y viceversa)? Un buen lugar por donde empezar son estos dos clásicos que sugiere Adam Kucharski https://twitter.com/AdamJKucharski/status/1340608427895250945
Para más información recomiendo la excelente nota de Apoorva Mandavilli que resume estos resultados: Los científicos deberían observar y preocuparse, sí, pero el resto de nosotros no debemos entrar en pánico. https://twitter.com/apoorva_nyc/status/1340672475617701900
¿Querés leer algunos hilos mucho mejores que este sobre la temática? Acá van algunos
https://twitter.com/BillHanage/status/1340332564721053696
https://twitter.com/GuptaR_lab/status/1340438927254167554
https://twitter.com/K_G_Andersen/status/1340457619534692352
https://twitter.com/JeremyFarrar/status/1340244494105649152 https://twitter.com/firefoxx66/status/1340359989395861506
https://twitter.com/BillHanage/status/1340332564721053696
https://twitter.com/GuptaR_lab/status/1340438927254167554
https://twitter.com/K_G_Andersen/status/1340457619534692352
https://twitter.com/JeremyFarrar/status/1340244494105649152 https://twitter.com/firefoxx66/status/1340359989395861506

 Read on Twitter
Read on Twitter